Nat Commun | 临床大队列血液蛋白组学揭示药物性肝损伤生物标志物
景杰生物 | 报道
药物性肝损伤 (DILI) 是指在正常治疗或临床剂量范围内的药物使用引起的肝脏损害。药物性肝损伤的诊断及其与其他肝病的区分是药物开发和临床实践中的重大挑战,但是目前的生物标志物无法将药物肝损伤与其他病因引起的急性肝损伤区分开。因此,需要一种新的能准确检测和诊断药物肝损伤的生物标志物。
长期保存,均保持有独特且稳定的蛋白表达谱,且临床化学检测之间有很强的相关性。因此与其他组学结果相比,血液蛋白质组学具有更稳定的结果及更高的临床转化价值,在临床疾病研究中发挥巨大应用价值[1]。
近日,诺丁汉大学Guruprasad P. Aithal团队在Nature Communications(IF=16.6)上发表“Tandem mass tag-based quantitative proteomic profiling identifies candidate serum biomarkers of drug-induced liver injury in humans[2]”的研究论文。该多中心病例对照研究利用蛋白质组学技术对血浆样本进行检测,筛选出了可以早期识别药物性肝损伤的生物标志物。研究者发现基于果糖-1,6-二磷酸酶1(FBP1)+谷胱甘肽S-转移酶A1(GSTA1)+白细胞来源趋化素2(LECT2)的蛋白预测模型可有效识别药物性肝损伤和其他继续肝损伤,助力药物肝损伤的早期发现及诊断。

在该研究中,患者被分为三个队列:发现队列(Discovery cohort),验证队列(Confirmatory cohort)和重复队列(Replication cohort)。每个队列中均包括发病时DILI患者(DO)和随访时DILI患者(DF),发病时其他急性肝损伤患者(NDO)和随访时其他急性肝损伤患者(NDF),非酒精性脂肪肝患者(NAFLD)以及健康对照(HV)。研究者在发现队列进行蛋白质组学分析筛选生物标志物;在验证队列使用质谱分析(MS)和ELISA验证结果;在重复队列中进一步验证生物标志物识别DILI的性能。
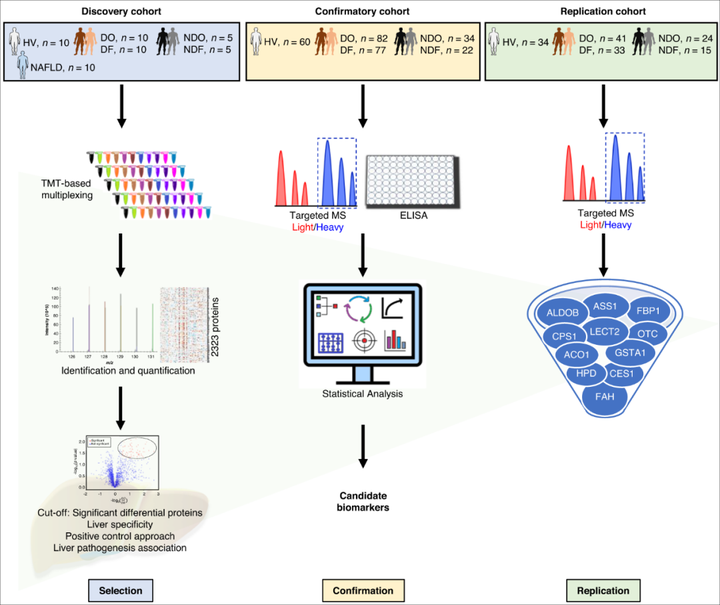
图1 药物性肝损伤生物标志物研究策略
1 发现队列蛋白质组学研究者采集了发现队列人群的血浆样本进行了蛋白质组学检测,共鉴定到2323种蛋白质,并进一步对不同实验组的蛋白组学结果进行了组间两两比较(DO vs HV,DO vs DF,NDO vs DO,NDO vs HV)。研究者共发现89种差异蛋白,有51种蛋白在至少两种组间比较结果中存在显著差异,并对这51种蛋白质进行了进一步研究。
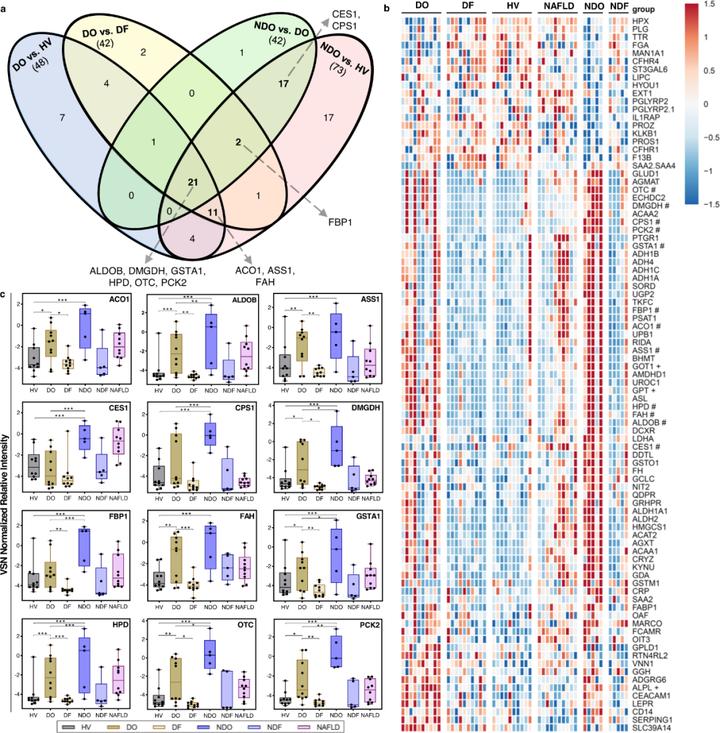
图2 蛋白质组学分析筛选生物标志物
2 区分药物性肝损伤和健康人群的生物标志物研究者进一步从差异表达倍数、肝脏特异性以及肝脏生物学的机制相关性等三个维度从51种蛋白质中筛选出13种蛋白作为候选生物标志物。研究者在验证队列以及复制队列中进一步使用logistic回归分析和随机森林(RF)方法构建模型寻找最佳的预测模型,并构建了4个预测模型,发现所有四种模型的AUC均 > 0.97。有趣的是,这些模型AUC的结果表现与单个蛋白质的AUC结果相当。 3 区分药物性肝损伤和其他急性肝损伤的生物标志物比较药物性肝损伤患者与其他急性肝损伤患者血液蛋白质组学结果时,研究者发现血清二磷酸果糖醛缩酶B(ALDOB)、血清氨基甲酰磷酸合酶(CPS1)、LECT2、鸟氨酸氨基甲酰转移酶(OTC)以及FBP1在两组间存在显著差异,FBP1在NDO患者中的表达显著更高,LECT2是唯一在DO中显著增加的蛋白质。研究者随后使用logistic回归分析和随机森林(RF)方法构建模型以区分DO和NDO,发现FBP1 + GSTA1 + LECT2 的组合模型性能最佳,该模型在识别DILI患者时特异性最高。
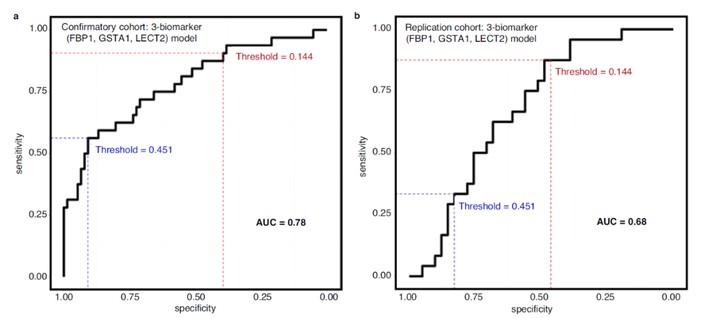
图3 最佳模型区分D0与ND0患者的性能
综上所述,研究者通过大型多中心病例对照研究,使用蛋白质组学技术以及后续的生信分析揭示了基于FBP1+GSTA1+LECT2的预测模型可以识别DILI和非DILI肝病,凸显出了蛋白质组学技术在DILI临床研究中的重要作用。

编者按:血液是临床中最为常用的检测样本,其中的蛋白质变化作为标志物可以指征多种疾病的发生和进展。从常规体检的谷丙转氨酶,到癌症诊断的AFP、CA125等蛋白指标,都为临床诊断提供了不可或缺的重要信息。此外,血液中还存在大量的糖基化蛋白,其中N-糖基化和O-糖基化是最常见的两种糖基化修饰类型,极大地拓宽了数据分析的维度,具有巨大的生物标志物研究潜力。近年来,随着质谱技术的进步,通过多组学技术来筛选新的血液标志物,已经成为了一个越来越重要的研究和转化应用的方向。
景杰生物推出基于高深度血液蛋白质组学+完整N糖肽+完整O-GalNAc的血液多组学生物标志物研究解决方案,特别适合于大规模队列样本的分析,为血液标志物筛选提供新的强大工具。详情可扫描文末的二维码或在微信后台留言或致电400-100-1145。
参考文献
1.Tebani, Abdellah et al. 2020. Integration of molecular profiles in a longitudinal wellness profiling cohort. Nature communications.
2. Ravindra KC, et al. 2023. Tandem mass tag-based quantitative proteomic profiling identifies candidate serum biomarkers of drug-induced liver injury in humans. Nature Communications.
景杰生物作为修饰组学领域的领跑者,拥有多种修饰抗体和修饰组学质谱检测服务。如果您想了解相关产品和服务的更多信息,请扫描下方二维码填写合作咨询表单、或咨询景杰生物销售工程师、或拨打科服热线400-100-1145。如有转载、投稿等其他合作需求,请在文章下方留言,或添加微信ptm-market咨询。


 浙公网安备 33010602011771号
浙公网安备 33010602011771号