关于python版本的infercnv
不看代码直接调包就是耍流氓
主要的思路:
cnv.pl.chromosome_heatmap内部核心操作:
use_rep = "cnv"
tmp_adata = AnnData(X=adata.obsm[f"X_{use_rep}"], obs=adata.obs)
这一步之后调用scanpy.pl.heatmap,内部再调用sc.tl.dendrogram
sc.tl.dendrogram(tmp_adata,groupby="histological.type.short")
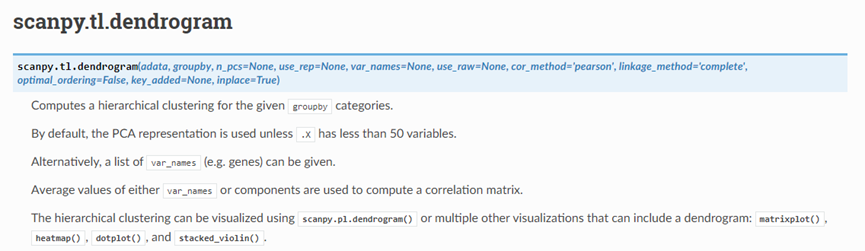
用新构建的对象去计算PCA,然后根据每个group的PCA的平均值计算组和组之间的pearson相关性,然后根据相关性去进行层次聚类。
一些其他的参数含义
_get_dendrogram_key 如果传进去的dendrogram没有计算好,这一步会进行一个计算。


 浙公网安备 33010602011771号
浙公网安备 33010602011771号